Evaluation Regression
Regressionsmodelle bewerten die Qualität ihrer Vorhersagen durch verschiedene Metriken. Das Bestimmtheitsmaß R², der Mean Absolute Error und die Residuenanalyse bilden das Fundament einer soliden Modellbewertung.
Inhaltsverzeichnis
- Übersicht der Regressionsmetriken
- Bestimmtheitsmaß (R²)
- Mean Absolute Error (MAE)
- Residual Plot (Residuenanalyse)
- Best Practices
- Zusammenfassung
- Abgrenzung zu verwandten Dokumenten
Übersicht der Regressionsmetriken
Bei der Evaluation von Regressionsmodellen stehen verschiedene Metriken zur Verfügung, die unterschiedliche Aspekte der Vorhersagequalität beleuchten.
flowchart TD
subgraph Metriken["📊 Regressionsmetriken"]
R2["R²<br/>Bestimmtheitsmaß"]
MAE["MAE<br/>Mean Absolute Error"]
MSE["MSE<br/>Mean Squared Error"]
RMSE["RMSE<br/>Root Mean Squared Error"]
end
subgraph Interpretation["🎯 Was sie messen"]
R2_INT["Erklärte Varianz<br/>0 bis 1"]
MAE_INT["Durchschnittlicher<br/>absoluter Fehler"]
MSE_INT["Durchschnittlicher<br/>quadratischer Fehler"]
RMSE_INT["Fehler in<br/>Originaleinheit"]
end
R2 --> R2_INT
MAE --> MAE_INT
MSE --> MSE_INT
RMSE --> RMSE_INT
style R2 fill:#4CAF50,color:#fff
style MAE fill:#2196F3,color:#fff
style MSE fill:#FF9800,color:#fff
style RMSE fill:#9C27B0,color:#fff
Bestimmtheitsmaß (R²)
Das Bestimmtheitsmaß ist ein statistisches Maß, das verwendet wird, um den Grad der Erklärungskraft eines Modells oder einer Regressionsanalyse zu quantifizieren.
Konzept
R² misst, wie gut die abhängige Variable durch die unabhängigen Variablen erklärt werden kann. Es beantwortet die Frage: Wie viel der Varianz in den Daten kann das Modell erklären?
flowchart LR
subgraph Modell["🔮 Regressionsmodell"]
X["Features X"]
Y["Zielvariable y"]
PRED["Vorhersage ŷ"]
end
subgraph R2_Calc["📐 R² Berechnung"]
VAR_TOTAL["Gesamtvarianz<br/>SS_total"]
VAR_RESIDUAL["Residualvarianz<br/>SS_residual"]
RESULT["R² = 1 - SS_res/SS_total"]
end
X --> PRED
Y --> VAR_TOTAL
PRED --> VAR_RESIDUAL
VAR_TOTAL --> RESULT
VAR_RESIDUAL --> RESULT
style RESULT fill:#4CAF50,color:#fff
Interpretation
| R²-Wert | Interpretation |
|---|---|
| 1.0 | Perfekte Erklärung – Modell erklärt 100% der Varianz |
| 0.8 - 1.0 | Sehr gute Erklärungskraft |
| 0.6 - 0.8 | Gute Erklärungskraft |
| 0.4 - 0.6 | Moderate Erklärungskraft |
| 0.0 - 0.4 | Schwache Erklärungskraft |
| < 0 | Modell schlechter als Mittelwert-Vorhersage |
[!WARNING] R² allein reicht nicht
Ein hoher R²-Wert garantiert kein gutes Modell. R² sollte immer in Verbindung mit anderen Metriken und einer Residuenanalyse betrachtet werden.
Mathematische Definition
Die Berechnung erfolgt über das Verhältnis von erklärter zu gesamter Varianz:
\[R^2 = 1 - \frac{SS_{residual}}{SS_{total}} = 1 - \frac{\sum_{i=1}^{n}(y_i - \hat{y}_i)^2}{\sum_{i=1}^{n}(y_i - \bar{y})^2}\]Wobei:
- $y_i$ = tatsächlicher Wert
- $\hat{y}_i$ = vorhergesagter Wert
- $\bar{y}$ = Mittelwert der tatsächlichen Werte
Implementation in Python
from sklearn.metrics import r2_score
from sklearn.linear_model import LinearRegression
from sklearn.model_selection import train_test_split
import numpy as np
# Beispieldaten
data = np.array([[1], [2], [3], [4], [5], [6], [7], [8], [9], [10]])
target = np.array([2.1, 4.2, 5.8, 8.1, 10.2, 11.9, 14.1, 16.0, 18.2, 20.1])
# Train-Test-Split
data_train, data_test, target_train, target_test = train_test_split(data, target, test_size=0.2, random_state=42)
# Modell trainieren
model = LinearRegression()
model.fit(data_train, target_train)
# Vorhersagen
target_pred = model.predict(data_test)
# R² berechnen
r2 = r2_score(target_test, target_pred)
print(f"R² Score: {r2:.4f}")
# R² für Trainings- und Testdaten vergleichen
r2_train = r2_score(target_train, model.predict(data_train))
r2_test = r2_score(target_test, target_pred)
print(f"R² Training: {r2_train:.4f}")
print(f"R² Test: {r2_test:.4f}")
Mean Absolute Error (MAE)
Der Mean Absolute Error ist eine häufig verwendete Metrik zur Bewertung der Genauigkeit von Vorhersagemodellen.
Konzept
MAE misst den durchschnittlichen absoluten Unterschied zwischen den tatsächlichen Werten und den vorhergesagten Werten. Er ist besonders nützlich, wenn Ausreißer in den Daten vorhanden sind, da er weniger empfindlich auf extreme Werte reagiert als andere Metriken.
flowchart TD
subgraph Berechnung["📊 MAE Berechnung"]
REAL["Tatsächliche<br/>Werte y"]
PRED["Vorhergesagte<br/>Werte ŷ"]
DIFF["Differenz<br/>|y - ŷ|"]
ABS["Absolutwerte<br/>bilden"]
MEAN["Mittelwert<br/>berechnen"]
MAE["MAE"]
end
REAL --> DIFF
PRED --> DIFF
DIFF --> ABS
ABS --> MEAN
MEAN --> MAE
style MAE fill:#2196F3,color:#fff
style MEAN fill:#64B5F6,color:#fff
Eigenschaften
| Eigenschaft | Beschreibung |
|---|---|
| Wertebereich | 0 bis ∞ (je kleiner, desto besser) |
| Einheit | Gleiche Einheit wie Zielvariable |
| Ausreißer | Weniger empfindlich als MSE |
| Interpretierbarkeit | Leicht verständlich |
Mathematische Definition
\[MAE = \frac{1}{n} \sum_{i=1}^{n} |y_i - \hat{y}_i|\]Vergleich MAE vs. MSE vs. RMSE
flowchart LR
subgraph Metriken["Fehlermetriken im Vergleich"]
MAE_BOX["**MAE**<br/>Mittlerer absoluter Fehler<br/>Robust gegen Ausreißer"]
MSE_BOX["**MSE**<br/>Mittlerer quadratischer Fehler<br/>Bestraft große Fehler stärker"]
RMSE_BOX["**RMSE**<br/>Wurzel des MSE<br/>Gleiche Einheit wie y"]
end
style MAE_BOX fill:#2196F3,color:#fff
style MSE_BOX fill:#FF9800,color:#fff
style RMSE_BOX fill:#9C27B0,color:#fff
| Metrik | Formel | Besonderheit |
|---|---|---|
| MAE | $\frac{1}{n}\sum|y-\hat{y}|$ | Robust gegen Ausreißer |
| MSE | $\frac{1}{n}\sum(y-\hat{y})^2$ | Bestraft große Fehler quadratisch |
| RMSE | $\sqrt{MSE}$ | Interpretierbar in Originaleinheit |
Implementation in Python
from sklearn.metrics import mean_absolute_error, mean_squared_error
import numpy as np
# Beispiel: Tatsächliche und vorhergesagte Werte
target_true = np.array([3.0, -0.5, 2.0, 7.0, 4.5])
target_pred = np.array([2.5, 0.0, 2.1, 7.8, 4.2])
# Metriken berechnen
mae = mean_absolute_error(target_true, target_pred)
mse = mean_squared_error(target_true, target_pred)
rmse = np.sqrt(mse)
print(f"MAE: {mae:.4f}")
print(f"MSE: {mse:.4f}")
print(f"RMSE: {rmse:.4f}")
Ausgabe:
MAE: 0.3800
MSE: 0.2120
RMSE: 0.4604
Wann welche Metrik verwenden?
flowchart TD
START["Welche Metrik<br/>verwenden?"]
OUTLIER{"Ausreißer<br/>vorhanden?"}
INTERPRET{"Einfache<br/>Interpretation<br/>wichtig?"}
PENALTY{"Große Fehler<br/>stark bestrafen?"}
MAE_CHOICE["✅ MAE<br/>verwenden"]
MSE_CHOICE["✅ MSE/RMSE<br/>verwenden"]
RMSE_CHOICE["✅ RMSE<br/>verwenden"]
START --> OUTLIER
OUTLIER -->|Ja| MAE_CHOICE
OUTLIER -->|Nein| PENALTY
PENALTY -->|Ja| MSE_CHOICE
PENALTY -->|Nein| INTERPRET
INTERPRET -->|Ja| RMSE_CHOICE
INTERPRET -->|Nein| MSE_CHOICE
style MAE_CHOICE fill:#4CAF50,color:#fff
style MSE_CHOICE fill:#FF9800,color:#fff
style RMSE_CHOICE fill:#9C27B0,color:#fff
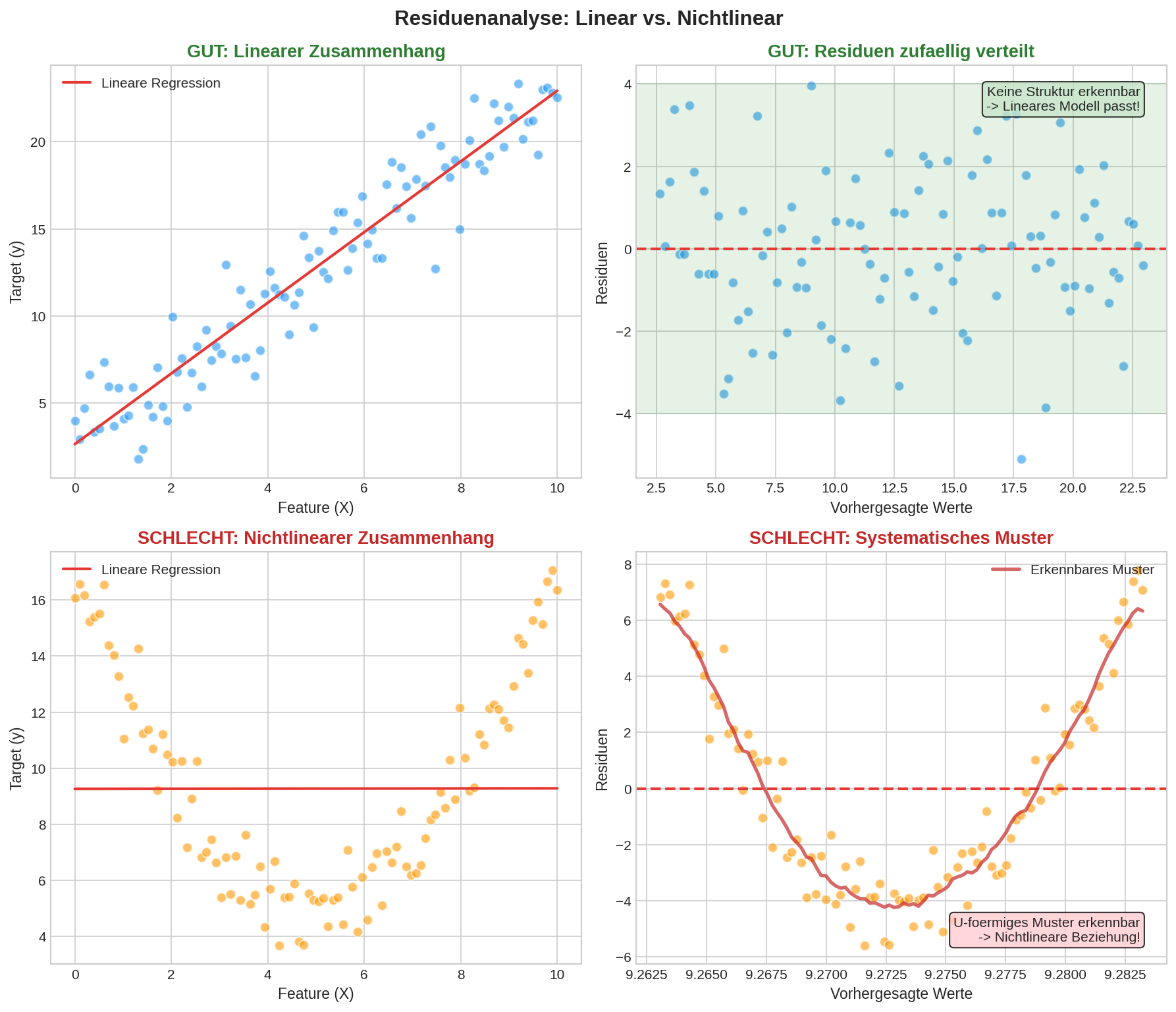
Residual Plot (Residuenanalyse)
Ein Residualplot ist eine statistische Analyse, die Unterschiede zwischen beobachteten und modellvorhergesagten Werten visualisiert.
Konzept
Residuen sind die Differenzen zwischen den tatsächlichen und den vorhergesagten Werten. Ein Residualplot zeigt diese Modellfehler und hilft bei der Diagnose von Modellproblemen.
\[Residuum = y_i - \hat{y}_i\]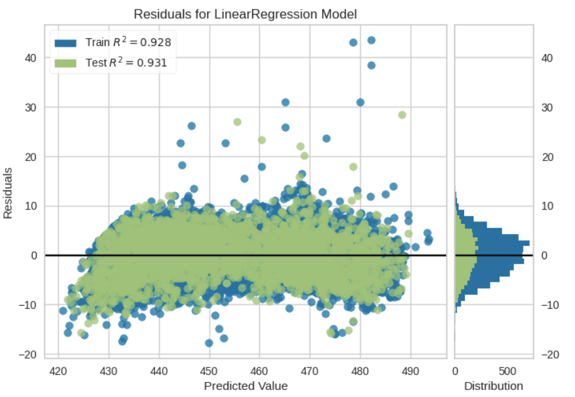
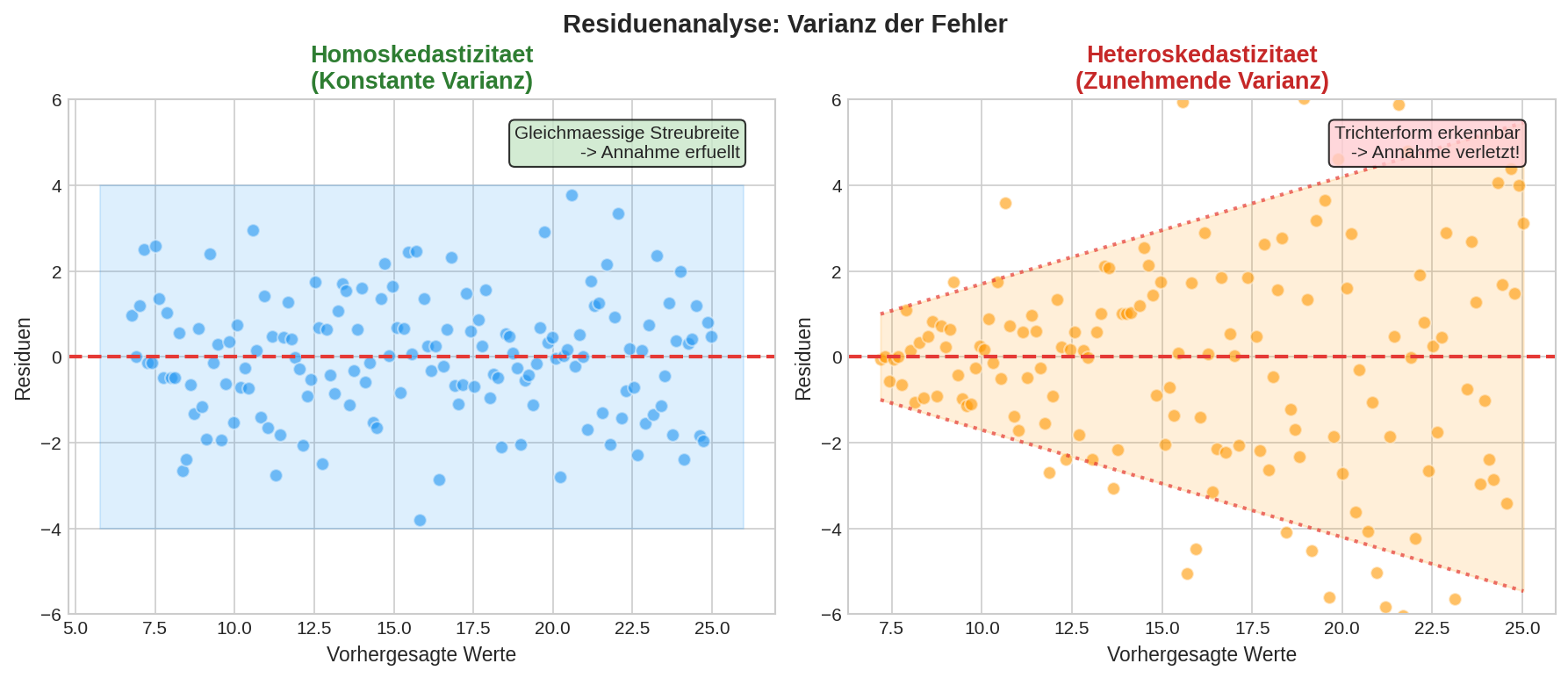
Interpretation von Residual Plots
| Muster | Bedeutung | Aktion |
|---|---|---|
| Zufällig um 0 | Modell erfasst Zusammenhang gut | ✅ Modell ist geeignet |
| Trichterform | Heteroskedastizität | Transformation der Zielvariable |
| Kurve/Bogen | Nicht-linearer Zusammenhang | Polynomiale Features hinzufügen |
| Cluster | Subgruppen in Daten | Separate Modelle oder zusätzliche Features |
Visuelle Muster erkennen
flowchart LR
subgraph Patterns["Residuen-Muster"]
RANDOM["🎲 Zufällig<br/>━━━━━━━━━━<br/>✅ Ideal"]
FUNNEL["📐 Trichter<br/>◁━━━━━━━▷<br/>⚠️ ungleiche Varianz"]
CURVE["〰️ Kurve<br/>⌒━━━━━━⌒<br/>⚠️ Nicht-linear"]
end
style RANDOM fill:#4CAF50,color:#fff
style FUNNEL fill:#FF9800,color:#fff
style CURVE fill:#f44336,color:#fff
Implementation in Python
import matplotlib.pyplot as plt
import numpy as np
from sklearn.linear_model import LinearRegression
from sklearn.model_selection import train_test_split
# Beispieldaten generieren
np.random.seed(42)
data = np.random.rand(100, 1) * 10
target = 2.5 * data.flatten() + np.random.randn(100) * 2
# Train-Test-Split
data_train, data_test, target_train, target_test = train_test_split(data, target, test_size=0.2, random_state=42)
# Modell trainieren
model = LinearRegression()
model.fit(data_train, target_train)
# Vorhersagen
target_pred_train = model.predict(data_train)
target_pred_test = model.predict(data_test)
# Residuen berechnen
residuals_train = target_train - target_pred_train
residuals_test = target_test - target_pred_test
# Residual Plot erstellen
fig, axes = plt.subplots(1, 2, figsize=(14, 5))
# Plot 1: Residuen vs. Vorhergesagte Werte
axes[0].scatter(target_pred_test, residuals_test, alpha=0.7, edgecolors='black')
axes[0].axhline(y=0, color='red', linestyle='--', linewidth=2)
axes[0].set_xlabel('Vorhergesagte Werte')
axes[0].set_ylabel('Residuen')
axes[0].set_title('Residual Plot')
axes[0].grid(True, alpha=0.3)
# Plot 2: Histogramm der Residuen
axes[1].hist(residuals_test, bins=15, edgecolor='black', alpha=0.7)
axes[1].axvline(x=0, color='red', linestyle='--', linewidth=2)
axes[1].set_xlabel('Residuen')
axes[1].set_ylabel('Häufigkeit')
axes[1].set_title('Verteilung der Residuen')
axes[1].grid(True, alpha=0.3)
plt.tight_layout()
plt.show()
Vollständige Evaluation mit allen Metriken
from sklearn.metrics import r2_score, mean_absolute_error, mean_squared_error
import numpy as np
def evaluate_regression(target_true, target_pred, dataset_name=""):
"""
Vollständige Evaluation eines Regressionsmodells.
Parameters:
-----------
target_true : array-like
Tatsächliche Werte
target_pred : array-like
Vorhergesagte Werte
dataset_name : str
Name des Datensatzes (z.B. 'Training' oder 'Test')
Returns:
--------
dict : Dictionary mit allen Metriken
"""
metrics = {
'R²': r2_score(target_true, target_pred),
'MAE': mean_absolute_error(target_true, target_pred),
'MSE': mean_squared_error(target_true, target_pred),
'RMSE': np.sqrt(mean_squared_error(target_true, target_pred))
}
print(f"\n{'='*40}")
print(f"Evaluation: {dataset_name}")
print(f"{'='*40}")
for metric, value in metrics.items():
print(f"{metric:6s}: {value:.4f}")
return metrics
# Anwendung
metrics_train = evaluate_regression(target_train, target_pred_train, "Training")
metrics_test = evaluate_regression(target_test, target_pred_test, "Test")
Best Practices
Checkliste für Regressions-Evaluation
- R² für Training und Test berechnen – Großer Unterschied deutet auf Overfitting hin
- MAE und RMSE vergleichen – Großer Unterschied deutet auf Ausreißer hin
- Residual Plot analysieren – Auf Muster und ungleiche Varianz prüfen
- Residuen auf Normalverteilung prüfen – Histogramm und Q-Q-Plot nutzen
- Cross-Validation durchführen – Stabilität der Metriken über Folds prüfen
Typische Fehler vermeiden
| Fehler | Problem | Lösung |
|---|---|---|
| Nur R² betrachten | Kann irreführend sein | Mehrere Metriken kombinieren |
| Train-Score als Maßstab | Overfitting übersehen | Test-Score priorisieren |
| Residuen ignorieren | Modellprobleme übersehen | Immer Residual Plot erstellen |
| Skala ignorieren | MAE/RMSE nicht vergleichbar | Auf Einheit der Zielvariable achten |
Zusammenfassung
flowchart TD
subgraph Evaluation["🎯 Regressions-Evaluation"]
R2["**R²**<br/>Erklärte Varianz<br/>0-1 (höher = besser)"]
MAE["**MAE**<br/>Mittlerer absoluter Fehler<br/>Robust gegen Ausreißer"]
RESIDUAL["**Residual Plot**<br/>Modelldiagnose<br/>Muster erkennen"]
end
subgraph Anwendung["📋 Anwendung"]
VERGLEICH["Modellvergleich"]
DIAGNOSE["Problemdiagnose"]
OPTIMIERUNG["Modelloptimierung"]
end
R2 --> VERGLEICH
MAE --> VERGLEICH
RESIDUAL --> DIAGNOSE
DIAGNOSE --> OPTIMIERUNG
style R2 fill:#4CAF50,color:#fff
style MAE fill:#2196F3,color:#fff
style RESIDUAL fill:#9C27B0,color:#fff
| Metrik | Stärke | Schwäche | |——–|——–|———-| | R² | Leicht interpretierbar, standardisiert | Kann bei nicht-linearen Zusammenhängen irreführen | | MAE | Robust gegen Ausreißer | Keine Bestrafung großer Fehler | | RMSE | Bestraft große Fehler, gleiche Einheit | Empfindlich gegen Ausreißer | | Residual Plot | Zeigt Modellprobleme visuell | Subjektive Interpretation |
Abgrenzung zu verwandten Dokumenten
| Thema | Abgrenzung |
|---|---|
| Bewertung: Klassifizierung | Regressions-Metriken (R2, MAE, RMSE) fuer kontinuierliche Werte; Klassifikations-Metriken (Precision, Recall) fuer Klassen |
| Overfitting | Regressions-Metriken messen Vorhersagefehler; Overfitting-Erkennung nutzt Train-Test-Vergleich dieser Metriken |
| Cross-Validation | Cross-Validation ist die Evaluierungsmethodik; Regressions-Metriken quantifizieren die Modellguete |
Version: 1.0
Stand: Januar 2026
Kurs: Machine Learning. Verstehen. Anwenden. Gestalten.